NG重磅 | 燕麦超级泛基因组
燕麦(Avena sativa)是全球第七大粮食作物,广泛应用于食品和饲料中,且因其高营养价值和较强的干旱适应性而具有重要的农业价值。燕麦属(Avena)包括约30个公认物种,涵盖二倍体(AA或CC)、四倍体(CCDD或AABB)和六倍体(AACCDD)等不同类型,展现出丰富的遗传多样性。尽管燕麦在全球农业中占据重要地位,但其基因组复杂、重复序列丰富,且研究资源有限,难以全面解析其遗传背景和进化历程。
河北大学生命科学学院杜会龙教授及其科研团队于2025年8月20号在著名期刊《Nature Genetics》上发表了一篇名为“Super-pangenome analyses across 35 accessions of 23 Avena species highlight their complex evolutionary history and extensive genomic diversity”的重要论文,构建了一个包含35个高质量基因组的超级泛基因组,通过系统发育分析揭示了燕麦属的起源与进化,特别是与抗逆性等重要性状相关的遗传资源,为燕麦的基因组学研究和分子育种提供了宝贵的基础。

一、栽培与野生燕麦的遗传多样性及基因组组装研究
为了选择代表性的栽培燕麦样本,作者基于1079个全球分布的燕麦样本的SNP构建了系统发育树,并结合群体结构、主成分分析PCA和地理分布,将其分为六大类。最终,选择了来自九个国家的14个代表性栽培燕麦样本,其中包括普通燕麦(A. sativa)和普通燕麦亚种(A. sativa ssp. nuda)。为了全面了解燕麦属的遗传多样性,作者还收集了21个野生燕麦物种,涵盖燕麦的二倍体、四倍体和六倍体基因组,展示了丰富的表型和遗传多样性。
在基因组组装方面,共采集了35个燕麦样本,对其中28个样本的基因组进行了全新构建,覆盖了不同的倍性和谱系。作者通过整合PacBio HiFi长读长序列、Hi-C数据和Illumina序列,成功实现了染色体级别的组装,生成了多个高质量的基因组。组装的基因组映射率达到99.89%,BUSCO评估完整性达到99.1%。作者进一步对这些基因组进行了详细的注释,转座元件占据了大部分基因组,长末端重复(LTR)是最丰富的类型。
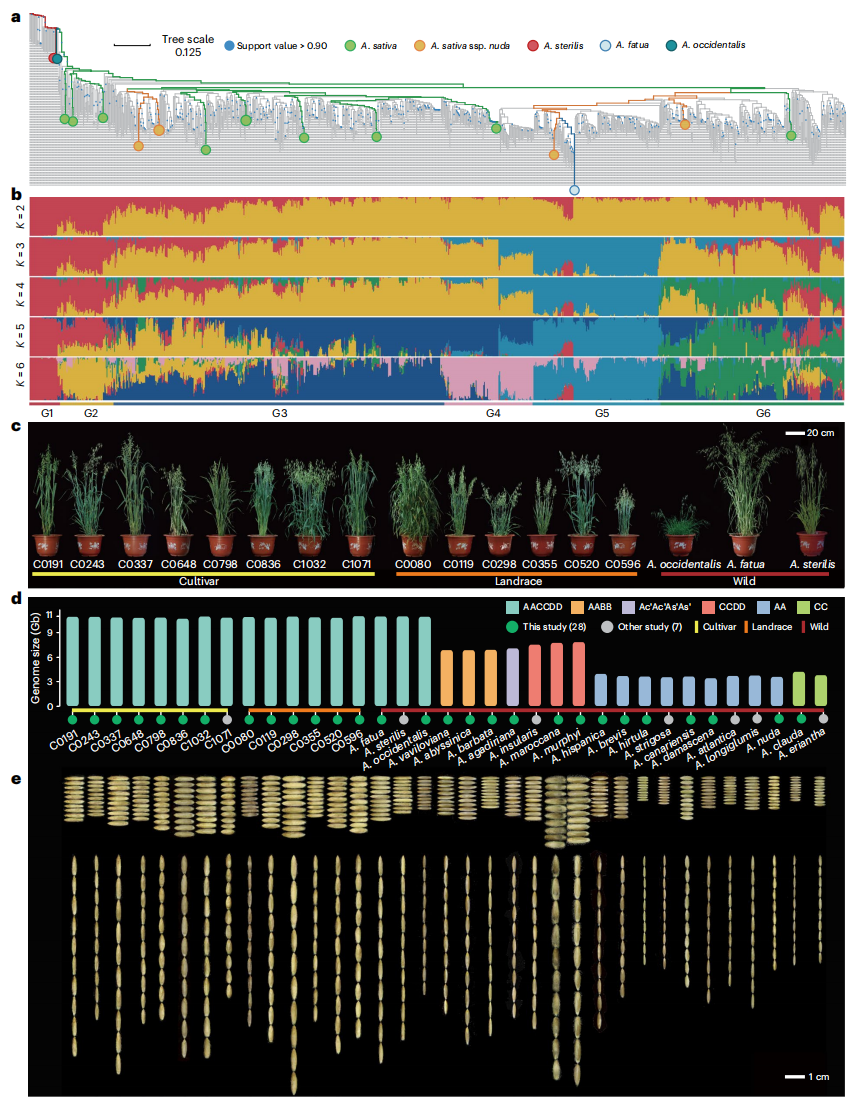
图1:栽培燕麦和燕麦属野生物种的系统发育、群体结构及多样化表型
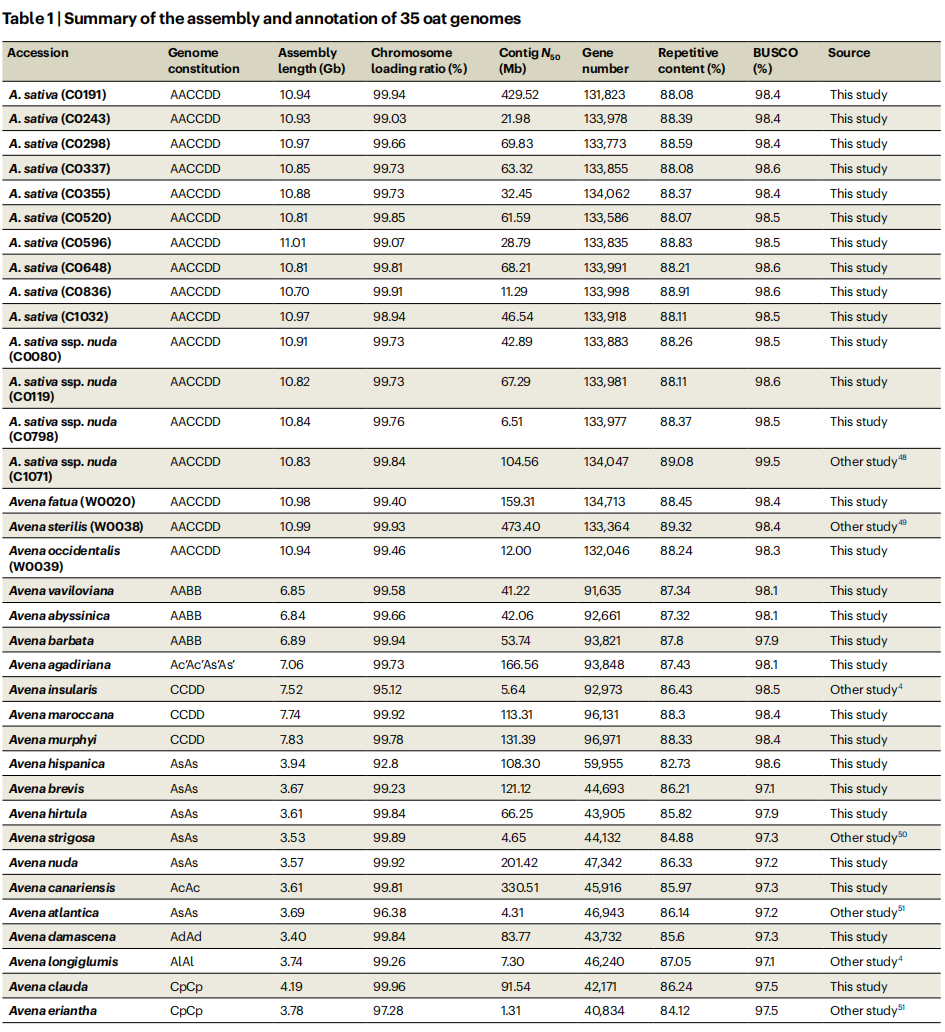
表1:35个燕麦属基因组的组装及注释
二、燕麦亚基因组的起源、进化与多倍体化历史
作者通过系统发育分析、k-mers模式和序列相似性,进一步阐明了燕麦属亚基因组的起源与进化历史。作者根据分析结果,将21个野生物种和2个栽培燕麦物种的亚基因组分为A、B、C、D四个谱系,其中A谱系大约在1087万年前分化,B谱系则在350万年前从A/D谱系分离,并在300万年前进一步分化。Avena hirtula虽然归类为As亚型,但与Ad/Ac物种的关系更为密切,这一结论通过同源分析和FISH实验得到了验证。
在祖先染色体重建中,作者发现四个谱系之间存在大规模基因组重排,表明多倍体化对基因组结构产生了显著影响。Avena agadiriana与传统的AABB物种在分类上存在显著差异,其亚基因组更接近Ac和As亚型物种,表明其并非典型的AABB物种。结合叶绿体和线粒体基因组分析,作者提出了燕麦属的进化模型:AABB四倍体起源于As与B二倍体杂交,约0.02-1.24百万年前;A. agadiriana由Ac与As二倍体杂交形成,约1.56-2.95百万年前;CCDD四倍体由C与D二倍体杂交,约0.43-4.99百万年前;六倍体物种则源于As/Al祖先与CCDD四倍体的杂交,时间约为0.23-0.73百万年前。研究还表明,A. fatua与栽培燕麦亲缘关系更为接近,重新界定了栽培燕麦的潜在祖先物种。
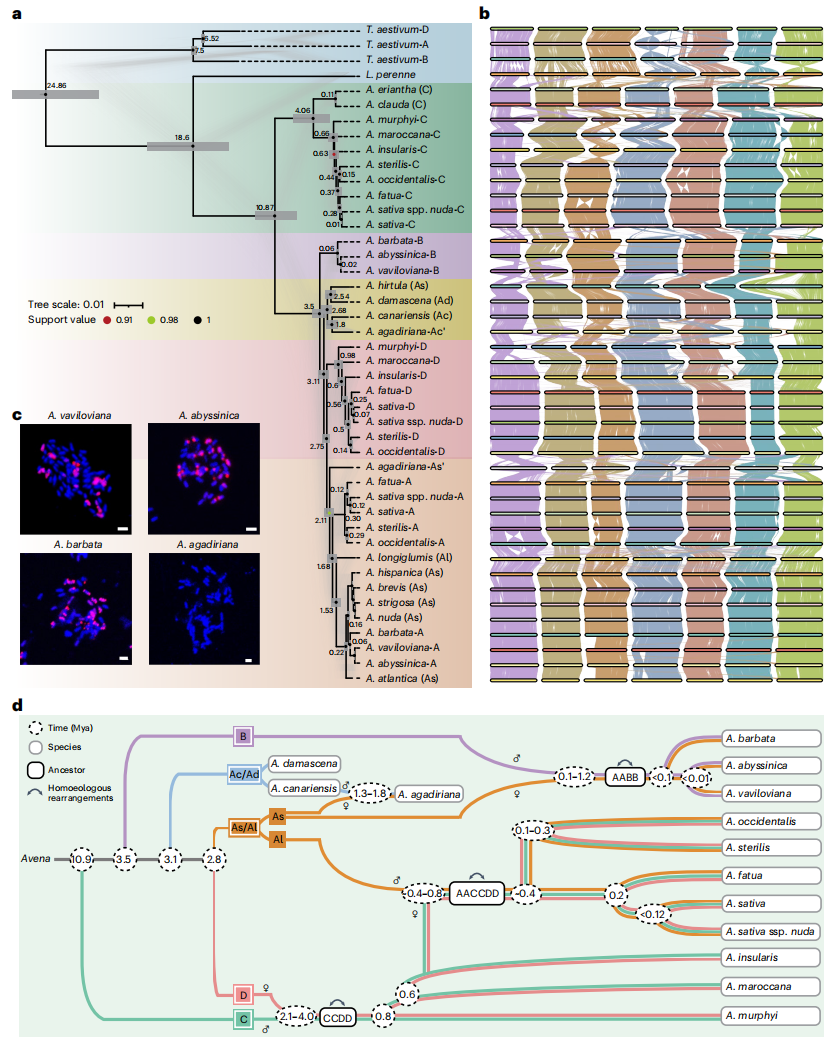
图2:燕麦的系统发育、起源和进化预测
三、燕麦属超级泛基因组的构建
作者构建了一个基于35份材料和76个(亚)基因组的燕麦属超级泛基因组,涵盖了75830个基因家族。研究发现,野生燕麦贡献了大量新的基因家族(20197个),这些基因在栽培燕麦中缺失,揭示了野生物种具有更高的遗传多样性。通过对六倍体和二倍体/四倍体燕麦A、C、D亚基因组的比较,发现不同亚基因组之间在基因功能和家族组成上存在显著差异,A亚基因组与抗病性和适应性相关,而D亚基因组则主要涉及植物器官发育。
此外,作者对野生和栽培燕麦的单倍型和基因家族进行了比较,发现野生燕麦具有更多的新基因和新单倍型,特别是在NBS、SSP和纤维素合酶等基因家族中,野生燕麦的基因增量显著。研究还发现,野生燕麦基因通过杂交渗入栽培燕麦,提高了其品质和抗性。例如,某些与环境适应和胁迫响应相关的基因在栽培燕麦中得到了显著改良。此研究为利用野生燕麦的遗传资源改良栽培燕麦提供了重要的遗传学证据,凸显了野生物种基因资源在燕麦改良中的巨大潜力。
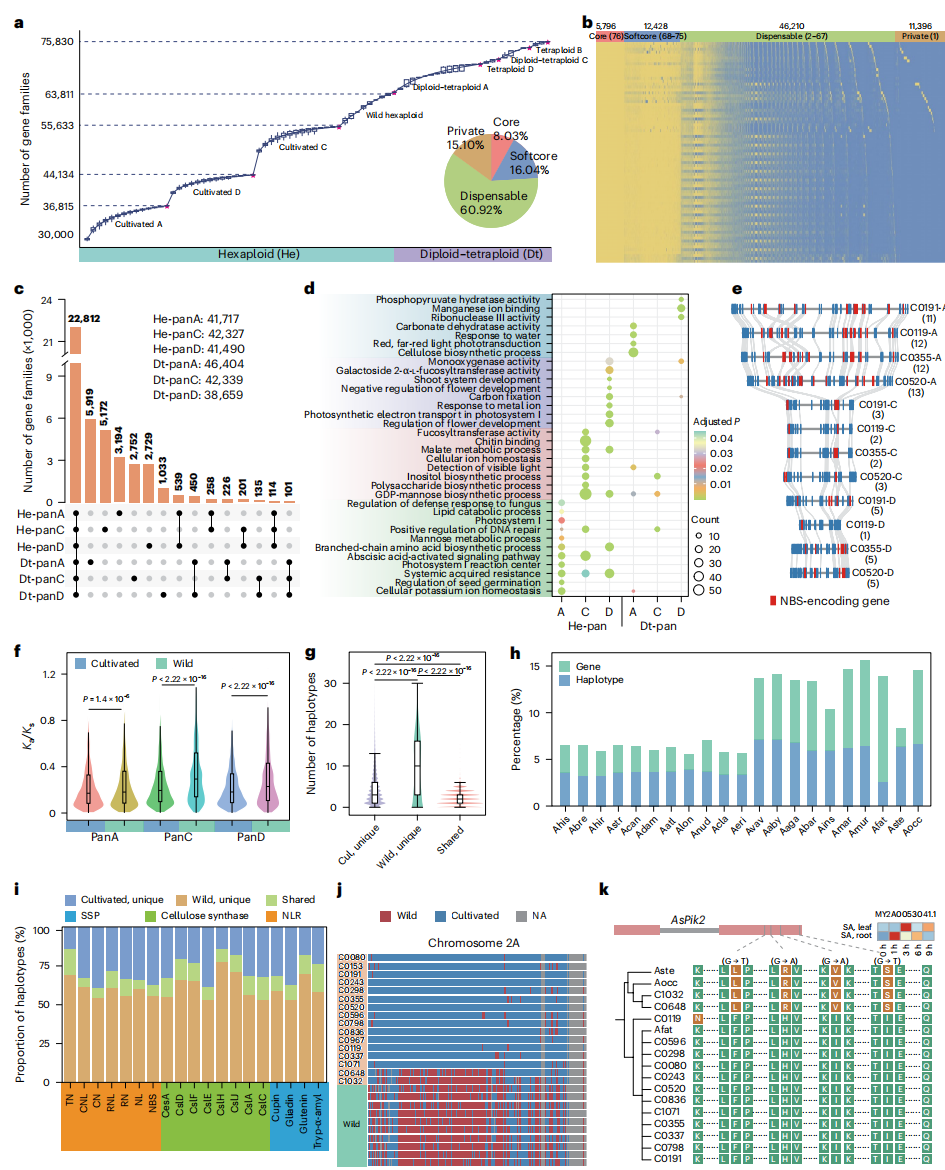
图3:燕麦属的超泛基因组和丰富的野生种特异遗传资源
四、17种六倍体燕麦中的结构变异分布
在16个六倍体燕麦基因组中,作者识别了超过137万个结构变异(SV),并进一步整合为555764个非冗余SV,包括插入、缺失、倒位和易位。大部分SV位于基因间区和基因边缘,且其密度随着距离基因区域的增大而增加。特别值得注意的是,SV与转座子(TE)高度重叠,其中Gypsy转座子最为丰富,且不同转座子家族在基因区域内外的分布差异显著。通过识别427个SV热点区域,作者揭示了与环境适应性密切相关的基因,这些基因涉及植物-病原相互作用和MAPK信号通路。其中,包含545个独立SV的热点区域还发现了与抗白粉病相关的NBS编码基因。研究结果表明,SV在燕麦的适应性进化中起着关键作用,提供了深入理解燕麦基因组变异与遗传多样性的重要资源。
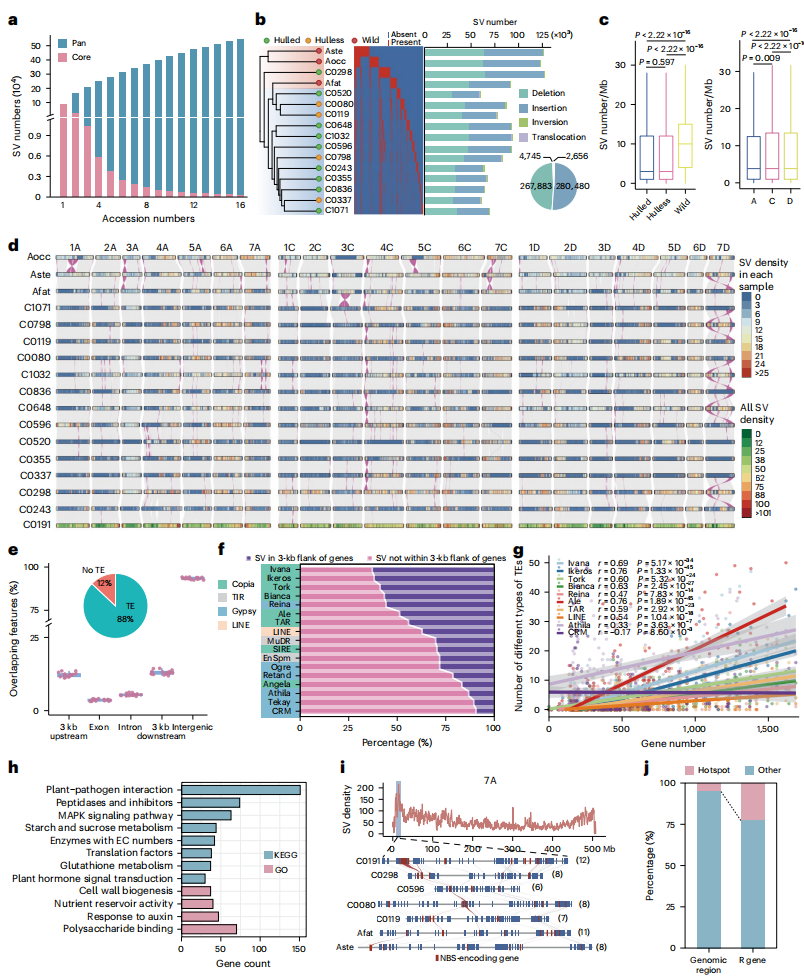
图4:17个六倍体燕麦的SVs特征
五、SV对燕麦在胁迫处理下基因表达的影响
作者通过对17份六倍体燕麦材料的1401个RNA测序样本进行分析,系统揭示了结构变异(SV)在基因表达调控和胁迫响应中的作用。结果显示,C亚基因组的整体表达水平普遍受到抑制,而A与D亚基因组在不同材料中呈现动态的优势切换,提示其在功能创新过程中可能经历了新功能化或亚功能化。作者共鉴定出70132个SV相关基因,这些基因整体表达量显著低于非SV基因,且更易沉默,其中位于编码区的SV对基因表达的影响尤为突出。进一步分析表明,在干旱、高温、盐和碱等胁迫条件下,SV基因的表达变化幅度显著高于非SV基因,表现出更强的环境敏感性。在各类胁迫处理中,作者共检测到约1.0-1.6万个差异表达基因,这些基因主要参与防御反应、脱落酸信号以及热休克蛋白结合等功能。此外,作者还鉴定出多个与SV显著关联的基因(如DRO1、OsGA2ox6、OsPRR73及OsVP1),并证实其在胁迫响应中发挥关键作用。
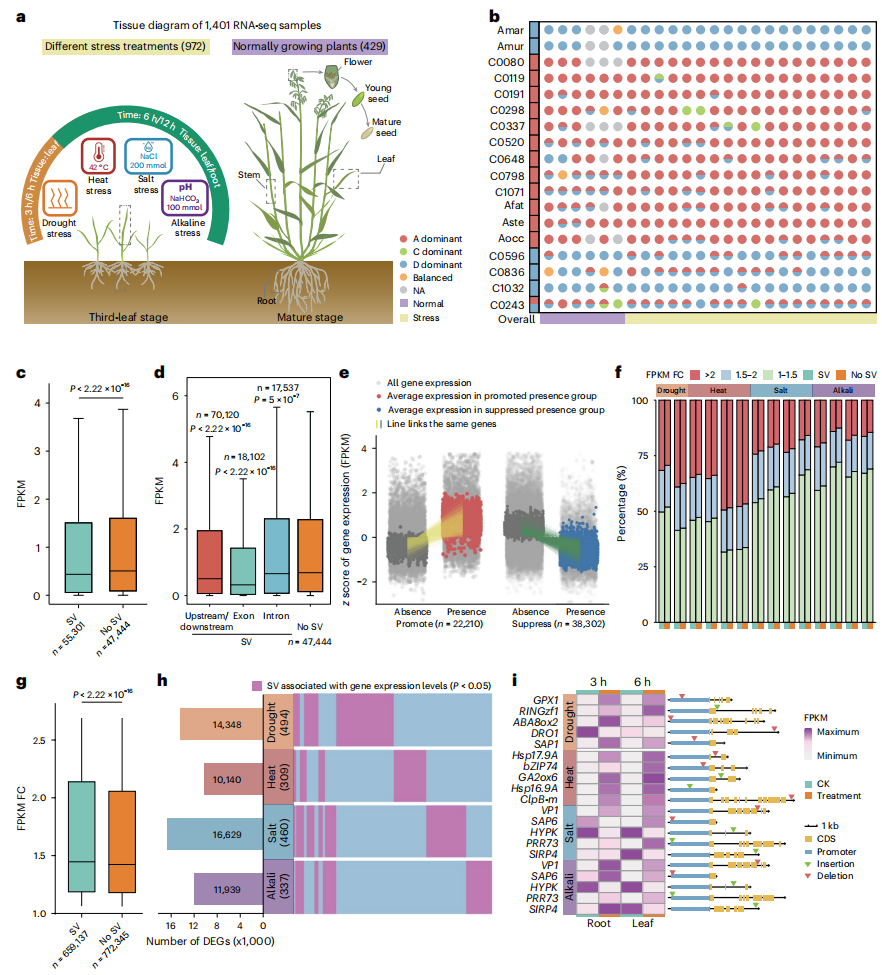
图5:SV对基因表达改变的影响
六、SVs对燕麦抗旱性的贡献
作者对186份燕麦材料进行基于结构变异(SV)和SNP的全基因组关联分析,鉴定出2223个与抗旱性相关的SV及3154个候选基因。结合表达谱和SV-eGene分析,作者进一步确认了13个显著候选基因。特别是,作者发现AsARF7基因附近的SV与抗旱性高度相关(P = 7.76 × 10⁻²³),且该SV在80%的高抗旱材料中存在。通过表型和转录组分析,作者证实该SV显著调控AsARF7的表达,从而影响抗旱性。功能验证结果显示,沉默AsARF7基因可增强燕麦的抗旱性,而过表达则削弱其耐旱能力。
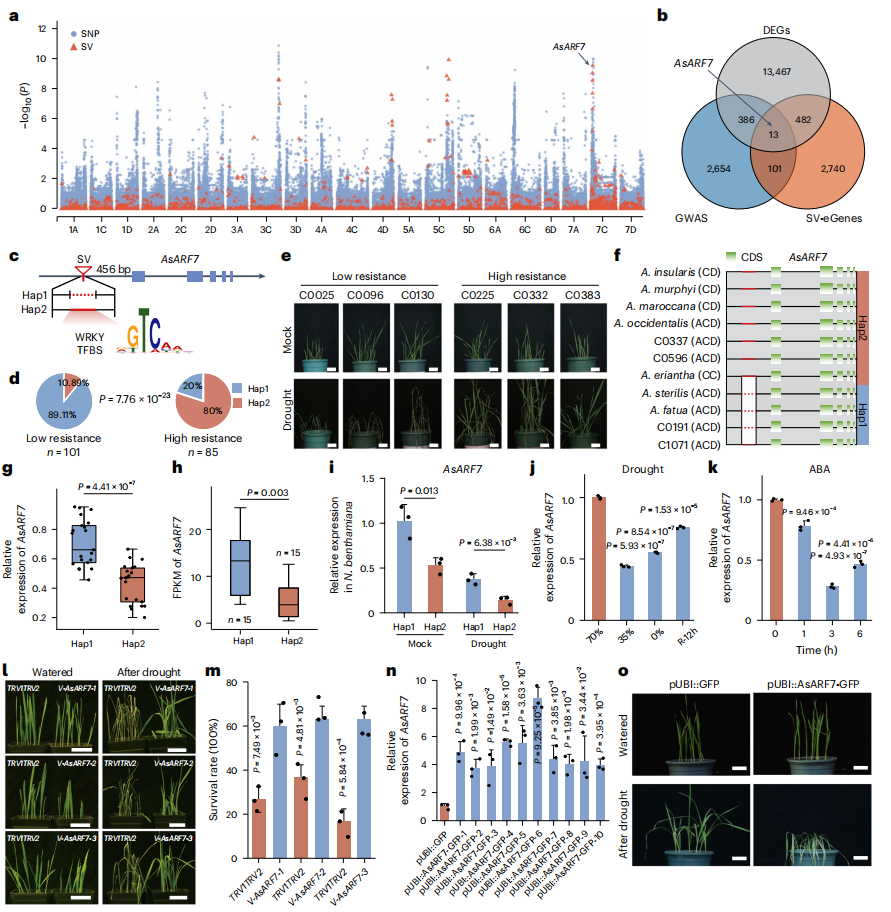
图6:基于SV-based GWAS的燕麦耐旱性关键SV及其相关基因的鉴定与验证
结语
作者通过构建覆盖23个燕麦物种、35个样本的燕麦超级泛基因组,系统解析了燕麦的系统发育、起源和多倍化历史,并揭示了A/C/D亚基因组在功能上的分化。相较于栽培型,野生燕麦显著扩展了遗传多样性,增加了26.63%的新基因家族和59.93%的新单倍型,为后续育种提供了重要资源。基于六倍体燕麦的结构变异(SV)图谱与多胁迫转录组分析,作者发现SV在胁迫条件下广泛调控基因表达。SV-GWAS分析还发现,含WRKY结合位点的顺式调控SV与抗旱性显著相关,并通过基因沉默/过表达与表型验证了该发现。该研究为燕麦育种提供了关键的分子工具和方法,推动了基因组学、表型学与环境适应性之间的深度关联。通过全面揭示基因家族、单倍型与结构变异的相互作用,为未来的燕麦改良和抗逆性提升提供了重要的理论基础。
华命生物产品服务一览
华命生物目前已开通微信公众号、抖音、知乎、B站、小红书等线上平台,欢迎感兴趣的老师扫码关注了解更多内容!